1. 切换任务

2. 基本设置更改

3. 图形参数更改

4. 图形颜色更改

5. 图片下载

1. 功能
用一个带有表头的表格数据绘制一个热图,用渐变颜色来展现数据在不同样本/分组中的变化规律。
2. 应用范围
适用于转录组、代谢组、蛋白、16S、单细胞、空间转录组、实验结果采集等所有适合画热图的数据。
3. 输入
文件格式:支持txt(制表符分隔)文本文件、csv(逗号分隔)文本文件、以及Excel专用的xlsx格式,同样支持旧版Excel的xls(Excel 97-2003 )格式。
数据格式:需提供矩阵文件(必须)和分组文件(可无)。
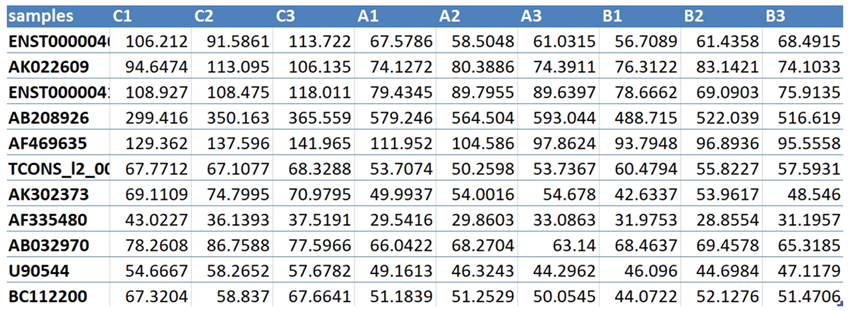
1)矩阵文件:文件为二维矩阵,第一行各列在热图横坐标从左到右排列,如样品名、物种名等;第一列各行在热图纵坐标上从上到下排列,如基因名、蛋白名等。矩阵行数不超过200,列数不超过50。
2)分组文件:为矩阵第一行的分组信息,例如当矩阵第一行为样品名时,可根据实际情况将各样品分为若干组,也可不分组。输入文件的数据与数据之间务必用制表符(tab符)隔开。
4. 部分重点参数说明
归一化:对数据进行Z-score处理,一般选择行,也可以选择列、行和列和不选择;
聚类:对行或列进行聚类,距离相近的将呈现在图片的相邻区域,横坐标或纵坐标的名称顺序将发生变化,视实际需要选择行、列、行和列或无;
名称显示:显示横坐标或纵坐标的名称,视实际需要选择行、列、行和列或无;
数值:是否在热图方格中显示对应数值;
方格形状:可选择矩形或圆形,默认矩形;
方格描边:选择热图格子描边有无,描边颜色粗细可自由调整;
图形颜色:改变图形整体渐变配色,提供发表级渐变色板自由选择,也可按自定义配色。
5. 输出
程序将按默认参数输出热图,使用者可根据个人需求进行参数调整,提供svg、pdf、png在内6种常用图片格式的文件下载。
6. 输出示例/效果参考
方格形状:矩形(图左)/圆形(图右)
方格尺寸:45W X 15W(Both)
方格描边:开(Both)
描边颜色:白(Both)
描边粗细:2(Both)
Q1.热图工具用什么方法进行归一化?
Z-score
Q2.提交为什么提示有重复?
热图第一列样本名不允许有重复,请参照提示查找重复的样本名,修改区分或删除
Q2.提交为什么提示超过行/列数?
动态热图矩阵行数不超过200,列数不超过50。
数据过多建议使用静态热图工具(点击跳转)
Q3. 为什么出图顺序跟文件不一样?
选择聚类,会改变横/纵坐标的排列顺序。
如果希望按照文档中的顺序出图,则在动态调整界面(设置——图形设置——聚类) 把聚类功能关掉即可。
Q5. 如何修改结果样式?
动态工具支持在线调整文字、颜色等样式,跳转至动态交互界面调整即可。
方式一:
工具页面下拉,即为调整界面,选择任务编号即可对任务进行修改。
方式二:
导航栏“我的项目”找到任务后,点击“跳转查看”,即可直达。
Q6.下载的结果文件用什么软件打开?
OmicShare云平台的结果文件(例如,下图为KEGG富集分析的结果文件)包括两种类型:图片文件和文本文件。
图片文件:
为了便于用户对图片进行后期编辑,OmicShare同时提供位图(png)和矢量图(pdf、svg)两种类型的图片。对于矢量图,最常见的是pdf和svg格式,常用Ai(Adobe illustrator)等进行编辑。其中,svg格式的图片可用网页浏览器打开,也可直接在word、ppt中使用。
文本文件:
文本文件的拓展名主要有4种类型:“.os”、“.xls”、“.log”和“.txt”。这些文件本质上都是制表符分隔的文本文件,使用记事本、Notepad++、EditPlus、Excel等文本编辑器直接打开即可。结果文件中,拓展名为“.os”文件为上传的原始数据;“.xls”文件一般为分析生成的数据表格;“.log”文件为任务运行日志文件,便于检查任务出错原因。
Q7. 提交的任务一直在排队怎么办?
提交任务后都需要排队,1分钟后,点击“任务状态刷新”按钮即可。除了可能需运行数天的注释工具,一般工具数十秒即可出结果,如果超出30分钟仍无结果,请联系OS客服,发送任务编号给OmicShare客服,会有专人为你处理任务问题。
Q8. 结果页面窗口有问题,图表加载不出来怎么办?
尝试用谷歌浏览器登录OmicShare查看结果文件,部分浏览器可能不兼容。
引用OmicShare Tools的参考文献为:
Mu, Hongyan, Jianzhou Chen, Wenjie Huang, Gui Huang, Meiying Deng, Shimiao Hong, Peng Ai, Chuan Gao, and Huangkai Zhou. 2024. “OmicShare tools: a Zero‐Code Interactive Online Platform for Biological Data Analysis and Visualization.” iMeta e228. https://doi.org/10.1002/imt2.228案例1:
发表期刊:Frontiers in cell and developmental biology
影响因子:5.5
发表时间:2021
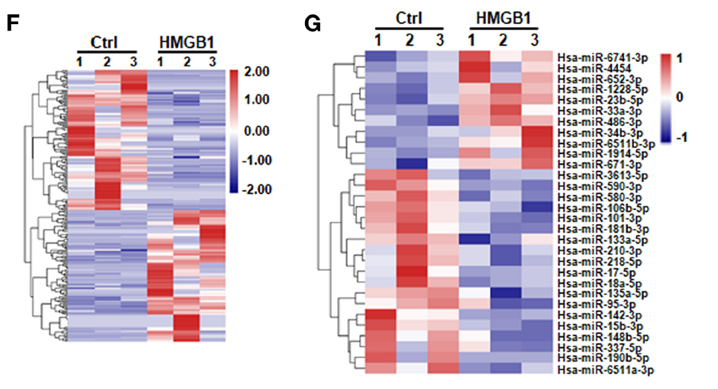
FIGURE 2. (F) Heatmap of lncRNA-seq analysis from a single GBM biopsy (GBM cells treated with 800 ng/ml rhHMGB1, n = 3; control GBM cells, n = 3). Two hundred and twenty-one lncRNAs were identified with a cut-off of >1.2-fold for gene expression change and p < 0.05. (G) Heatmap of miRNA-seq analysis from a single GBM biopsy (GBM cells treated with 800 ng/ml rhHMGB1, n = 3; control GBM cells, n = 3).
引用方式:Data analysis was performed using the OmicShare tools at www.omicshare.com/tools.
参考文献:
Gao X Y, Zang J, Zheng M H, et al. Temozolomide treatment induces HMGB1 to promote the formation of glioma stem cells via the TLR2/NEAT1/Wnt pathway in glioblastoma[J]. Frontiers in cell and developmental biology, 2021, 9: 620883.
案例2:
发表期刊:Journal of Cellular Physiology
影响因子:5.6
发表时间:2022
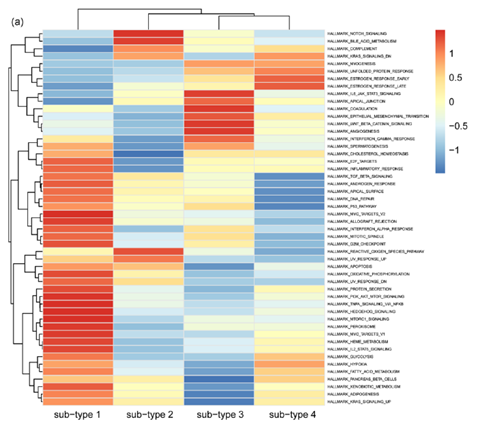
FIGURE 5 Enrichment analysis identifies Schwann cell subtype characteristics. (a) Gene set variation analysis (GSVA) enrichment analysis of hallmark gene sets in Schwann cell subtypes. Red color represents upregulation and blue color represents downregulation.
引用方式:We thank GENE DENOVO Company for bioinformatics analysis support with OmicShare Analysis Platform (http://www.omicshare.com/tools).
参考文献:
Zhang R, Chen Q, Huang L, et al. Single‐cell analyses reveal the differentiation shifts of Schwann cells in neonatal rat sciatic nerves[J]. Journal of Cellular Physiology, 2022, 237(1): 637-646.
案例3:
发表期刊:Journal of Hazardous Materials
影响因子:13.6
发表时间:2023
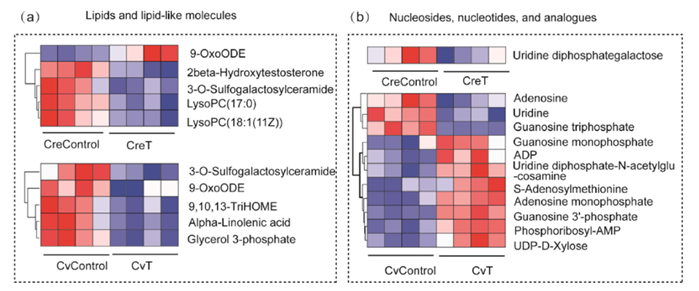
引用方式:and a differential metabolite (DEM) heat map were performed using the OmicShare bioinformatics learning platform (www.omicshare.com/tools).
Fig. 4. Effects of tritium exposure on expression patterns of nucleotides, carbohydrates, and amino acids.
参考文献:
Huang Y, Qin M, Lai J, et al. Assessing OBT formation and enrichment: ROS signaling is involved in the radiation hormesis induced by tritium exposure in algae[J]. Journal of Hazardous Materials, 2023, 443: 130159.
案例4:
发表期刊:EBioMedicine
影响因子:11.1
发表时间:2022
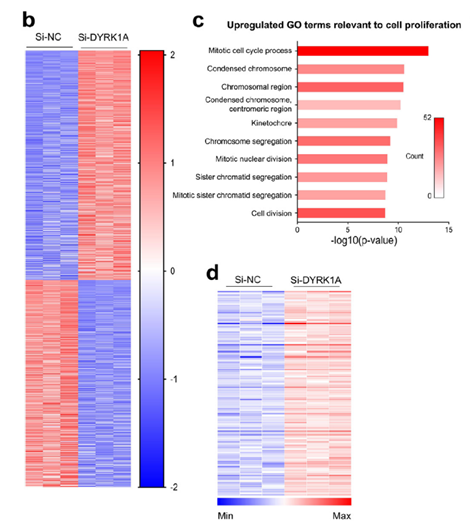
Figure 2. DYRK1A knockdown induces transcriptional reprogramming of networks that govern cardiomyocyte cell cycle activation. (b) Heatmap profile of RNA-sequencing (RNA-seq) analysis to show differentially expressed genes in primary neonatal cardiomyocytes transfected with scramble (si-NC) or DYRK1A siRNA (si-DYRK1A) (n=3 samples per group). (c) Gene ontology (GO) analysis of upregulated genes in si-DYRK1A cardiomyocytes (relative to si-NC group) show multiple, significantly enriched GO terms relevant to cell proliferation. (d) Heatmap profile of upregulated cell cycle regulators (relative to si-NC group).
引用方式:Heatmaps of gene expression, gene ontology (GO) and Kyoto encyclopedia of genes and genomes (KEGG) pathway analyses were performed using the OmicShare tools, a free online platform for data analysis (http://www.omicshare.com/tools).
参考文献:
Lan C, Chen C, Qu S, et al. Inhibition of DYRK1A, via histone modification, promotes cardiomyocyte cell cycle activation and cardiac repair after myocardial infarction[J]. EBioMedicine, 2022, 82.
案例5
发表期刊:Horticulture Research
影响因子:8.7
发表时间:2022
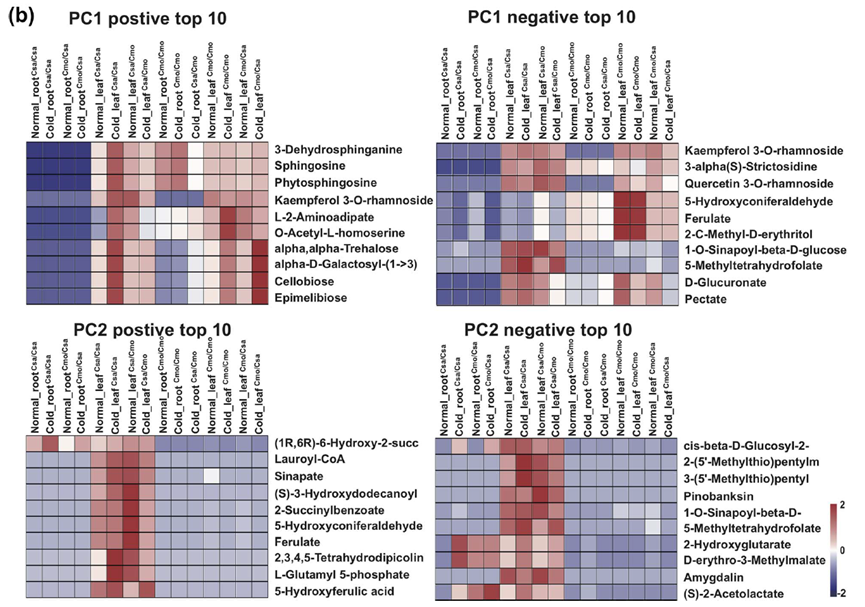
Figure 2. b Top 10 metabolites from the positive and negative loadings of PC1 and PC2, respectively.
引用方式:
Heatmaps of the top 10 metabolites from PC1 and PC2 were produced from ion intensity data using the online OmicShare Heatmap tools (http://www.omicshare.com/tools).
参考文献:
Liu W, Wang Q, Zhang R, et al. Rootstock–scion exchanging mRNAs participate in the pathways of amino acid and fatty acid metabolism in cucumber under early chilling stress[J]. Horticulture Research, 2022, 9: uhac031.




 扫码支付更轻松
扫码支付更轻松