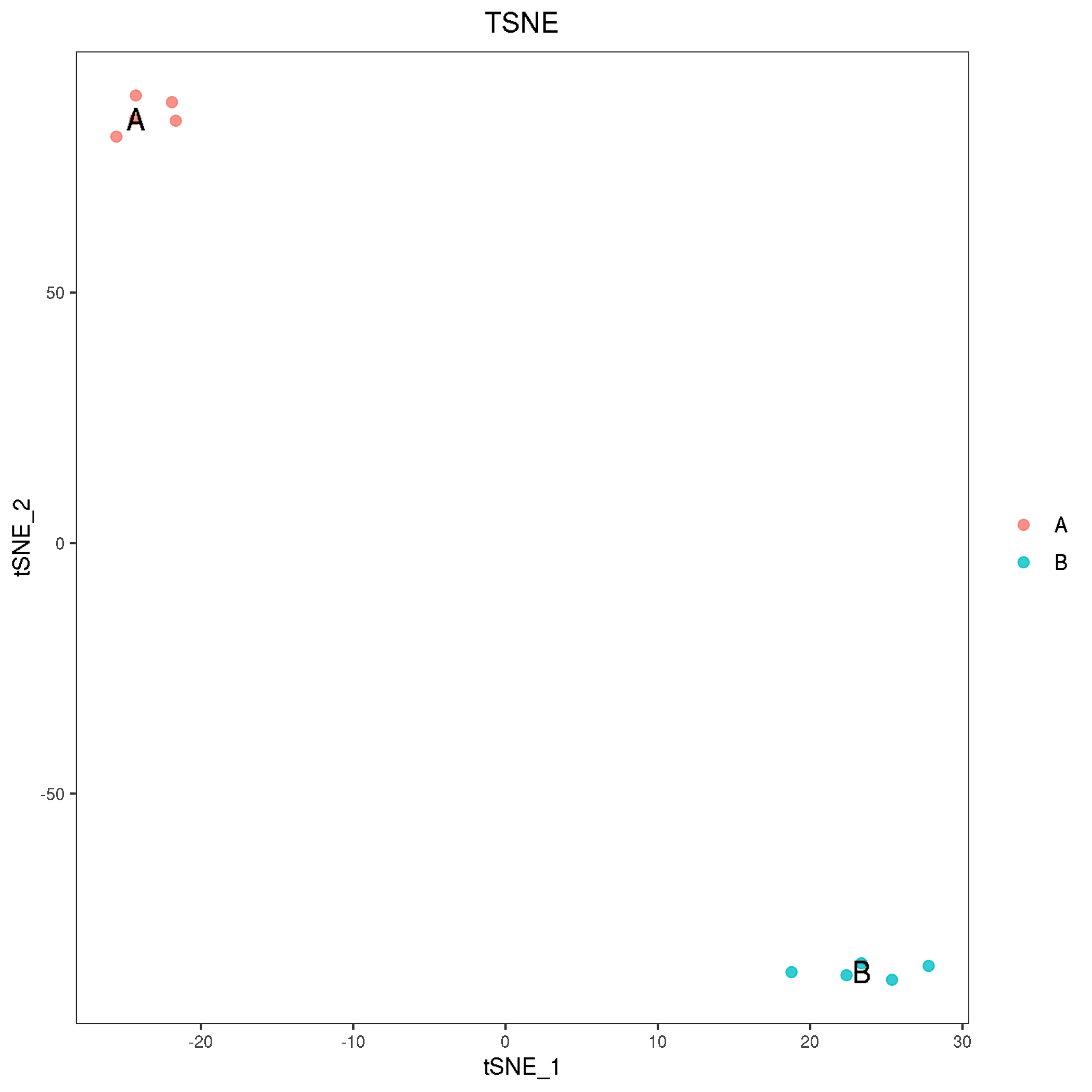
tSNE图是指经过非线性降维算法t分布随机邻接嵌入(t-distributed Stochastic Neighbor Embedding, tSNE)将高纬度数据投影到二维坐标系中绘制完成的图。tSNE图可以克服线性降维分类效果差的缺点,对数据完成更好的聚类分析。该工具暂不支持单细胞数据。
功能:
将包含多个变量的复杂数据,通过非线性降维的方式投影至二维平面,将相似度较高的个体聚类为同一亚群。注:该工具暂不支持单细胞数据。
输入文件:
丰度矩阵表格:文件为二维矩阵文件,第一行一般为基因ID或OTU,第一列一般为样本名称
分组文件:分组文件第一列为样本名称,第二列为分组名称,相同分组名称的样本被归为同一组。组别是绘图的着色依据。若无分组文件则使用样本名称做为着色依据。
参数:
(1)线性降维:线性降维是对数据的预处理,利用主成分对数据进行tSNE降维,可以有效提高tSNE算法的运算速度。使用partial_PCA算法后运算速度最快,但降维后的精确度最低,建议仅大型数据时使用。PCA算法和partial_PCA算法不可同时使用。
(2)归一化:我们利用z-score进行数据的归一化,即将每个基因的表达量减去这个基因在所有样本中表达量的均值,然后除以其标准差。对数据进行归一化,可消除表达量异常高的基因的影响,减少数据间的“贫富差距”。我们推荐对数据进行归一化。
(3)点密度为预设的数据复杂程度,决定了每个点附近最多相邻点的数量,在样本较多时,可适当降低点密度使聚类效果更清晰;在样本较少时,可提高点密度使分群内部的点更集中。
(4)选择行列绘图:选择行时以一行的数据为一个降维数据点进行绘图,选择列是以一列的数据为一个降维数据点进行绘图,当选择项与分组文件的样本名称不同时会导致绘图失败。
输出:
TSNE.xls:样本在tSNE二维图中的坐标位置
TSNE.png(pdf):样本降维得到的tSNE图,png格式为位图,pdf格式为矢量图,默认输出tSNE1-tSNE2降维图
输入的文件支持txt(制表符分隔)文本文件、csv(逗号分隔)文本文件、以及Excel专用的xlsx格式,同样支持旧版Excel的xls(Excel 97-2003 )格式。
输入:
1. 丰度矩阵表格
|
Samples |
Otu000005 |
Otu000003 |
Otu000011 |
Otu000001 |
Otu000002 |
|
A-1 |
28341 |
8364 |
15894 |
247 |
85 |
|
A-2 |
18513 |
9906 |
22261 |
390 |
133 |
|
A-3 |
22002 |
10373 |
22096 |
528 |
208 |
|
A-4 |
22164 |
12623 |
13696 |
459 |
211 |
|
A-6 |
24334 |
13724 |
3705 |
543 |
232 |
|
B-2 |
982 |
9484 |
88 |
15798 |
12886 |
|
B-3 |
918 |
9253 |
391 |
15569 |
13742 |
|
B-4 |
945 |
10204 |
300 |
16832 |
16816 |
|
B-5 |
802 |
9254 |
75 |
13295 |
14057 |
|
B-6 |
833 |
8786 |
200 |
12798 |
10805 |
2. 分组文件
|
A-1 |
A |
|
A-2 |
A |
|
A-3 |
A |
|
A-4 |
A |
|
A-6 |
A |
|
B-2 |
B |
|
B-3 |
B |
|
B-4 |
B |
|
B-5 |
B |
|
B-6 |
B |
输出:
1. 样本坐标表格
|
samples |
groups |
tSNE_1 |
tSNE_2 |
|
A-1 |
A |
-21.65079567 |
84.29810986 |
|
A-2 |
A |
-24.276575 |
89.32886812 |
|
A-3 |
A |
-21.90623727 |
87.98581002 |
|
A-4 |
A |
-24.30854873 |
84.6331113 |
|
A-6 |
A |
-25.55152121 |
81.11511 |
|
B-2 |
B |
23.36802676 |
-83.87482244 |
|
B-3 |
B |
22.39161677 |
-86.26611549 |
|
B-4 |
B |
18.7772739 |
-85.64608858 |
|
B-5 |
B |
25.3749806 |
-87.170141 |
|
B-6 |
B |
27.78177984 |
-84.4038418 |
2. 样本tSNE图
Q1. 上传的数据需要保存成什么格式?文件名称和拓展名有没有要求?
OmicShare当前支持txt(制表符分隔)文本文件、csv(逗号分隔)文本文件、以及Excel专用的xlsx格式,同样支持旧版Excel的xls(Excel 97-2003 )格式。如果是核酸、蛋白序列文件,必须为FASTA格式(本质是文本文件)。
文件名可由英文和数字构成,文件拓展名没有限制,可以是“.txt”、“.xlsx”、“.xls”、“.csv”“.fasta”等,例如 mydata01.txt,gene02.xlsx 。
Q2. 提交时报错常见问题:
1.提交时显示X行X列空行/无数据,请先自查表格中是否存在空格或空行,需要删掉。
2.提交时显示列数只有1列,但表格数据不止1列:列间需要用分隔符隔开,先行检查文件是否用了分隔符。
其它提示报错,请先自行根据提示修改;如果仍然无法提交,可通过左侧导航栏的“联系客服”选项咨询OmicShare客服。
Q3. 提交的任务完成后却不出图该怎么办?
主要原因是上传的数据文件存在特殊符号所致。可参考以下建议逐一排查出错原因:
(1)数据中含中文字符,把中文改成英文;
(2) 数据中含特殊符号,例如 %、NA、+、-、()、空格、科学计数、罗马字母等,去掉特殊符号,将空值用数字“0”替换;
(3)检查数据中是否有空列、空行、重复的行、重复的列,特别是行名(一般为gene id)、列名(一般为样本名)出现重复值,如果有删掉。
排查完之后,重新上传数据、提交任务。如果仍然不出图,可通过左侧导航栏的“联系客服”选项咨询OmicShare客服。
Q4.下载的结果文件用什么软件打开?
OmicShare云平台的结果文件(例如,下图为KEGG富集分析的结果文件)包括两种类型:图片文件和文本文件。
图片文件:
为了便于用户对图片进行后期编辑,OmicShare同时提供位图(png)和矢量图(pdf、svg)两种类型的图片。对于矢量图,最常见的是pdf和svg格式,常用Ai(Adobe illustrator)等进行编辑。其中,svg格式的图片可用网页浏览器打开,也可直接在word、ppt中使用。
文本文件:
文本文件的拓展名主要有4种类型:“.os”、“.xls”、“.log”和“.txt”。这些文件本质上都是制表符分隔的文本文件,使用记事本、Notepad++、EditPlus、Excel等文本编辑器直接打开即可。结果文件中,拓展名为“.os”文件为上传的原始数据;“.xls”文件一般为分析生成的数据表格;“.log”文件为任务运行日志文件,便于检查任务出错原因。
Q5. 提交的任务一直在排队怎么办?
提交任务后都需要排队,1分钟后,点击“任务状态刷新”按钮即可。除了可能需运行数天的注释工具,一般工具数十秒即可出结果,如果超出30分钟仍无结果,请联系OS客服,发送任务编号给OmicShare客服,会有专人为你处理任务问题。
Q6. 结果页面窗口有问题,图表加载不出来怎么办?
尝试用谷歌浏览器登录OmicShare查看结果文件,部分浏览器可能不兼容。




 扫码支付更轻松
扫码支付更轻松


