功能:
利用富集分析结果绘制富集分析条形图。
输入:
输入文件有两种种类型:
Type1:有5列数据,这5列分别是:
1.通路名称/term 名称/基因ID;
2.富集在该term/通路的目标基因/差异基因数目;
3.富集分析的P值(或Q值);(列名必须小写,即pvalue/qvalue)
4.(差异基因/目标基因)属于这个通路/term的基因数占总差异/目标基因数目的百分比;
5.前景基因(富集在该通路/term的差异基因/目标基因)占背景基因(富集在该通路/term的所有基因)的比例。
表格如下表所示:
|
id |
num |
qvalue |
per |
ratio |
|
DOID:0050687 cell type cancer |
499 |
4.38E-09 |
29.685 |
0.407 |
|
DOID:14566 disease of cellular proliferation |
1243 |
6.98E-07 |
73.944 |
0.352 |
|
DOID:0050686 organ system cancer |
845 |
6.98E-07 |
50.268 |
0.369 |
|
DOID:162 cancer |
1229 |
1.10E-06 |
73.111 |
0.352 |
|
DOID:17 musculoskeletal system disease |
360 |
1.20E-06 |
21.416 |
0.41 |
|
DOID:3996 urinary system cancer |
180 |
2.81E-06 |
10.708 |
0.457 |
|
DOID:1287 cardiovascular system disease |
408 |
5.18E-06 |
24.271 |
0.398 |
|
DOID:305 carcinoma |
281 |
1.12E-05 |
16.716 |
0.417 |
|
DOID:1749 squamous cell carcinoma |
237 |
1.53E-05 |
14.099 |
0.426 |
|
DOID:1909 melanoma |
235 |
3.38E-05 |
13.98 |
0.423 |
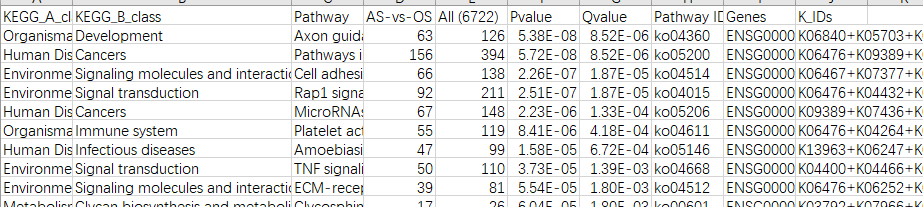
Type2:基迪奥流程结果绘图
KEGG数据:
GO数据: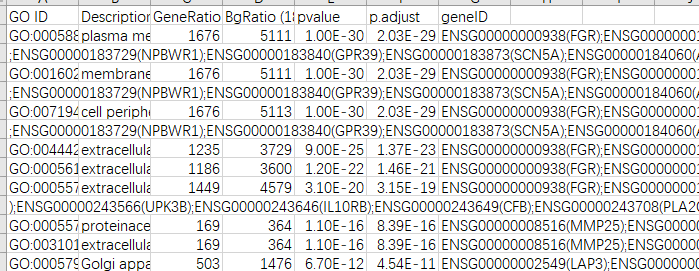
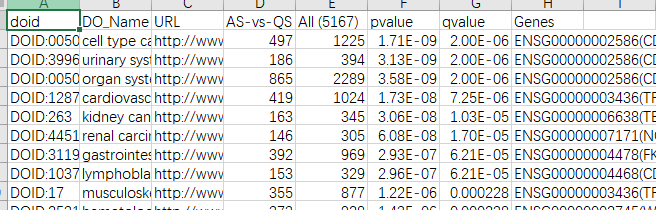
DO数据库:
Reactome数据库:

参数:
1.输入文件类型:type1类型的文件只有5列,type3类型的文件为基迪奥流程的文件;
2.用于作图的行:默认为前20行的数据用来作图;
3.参数选择:选择P-value或Q-value会影响最后的图形结果;
4. 顺序:条形图排列顺序,P/Q值从小到大排列绘图或P/Q值从大到小排列绘图;
5. 类型:富集分析类型,GO、KO、DO、Reactome
输出:
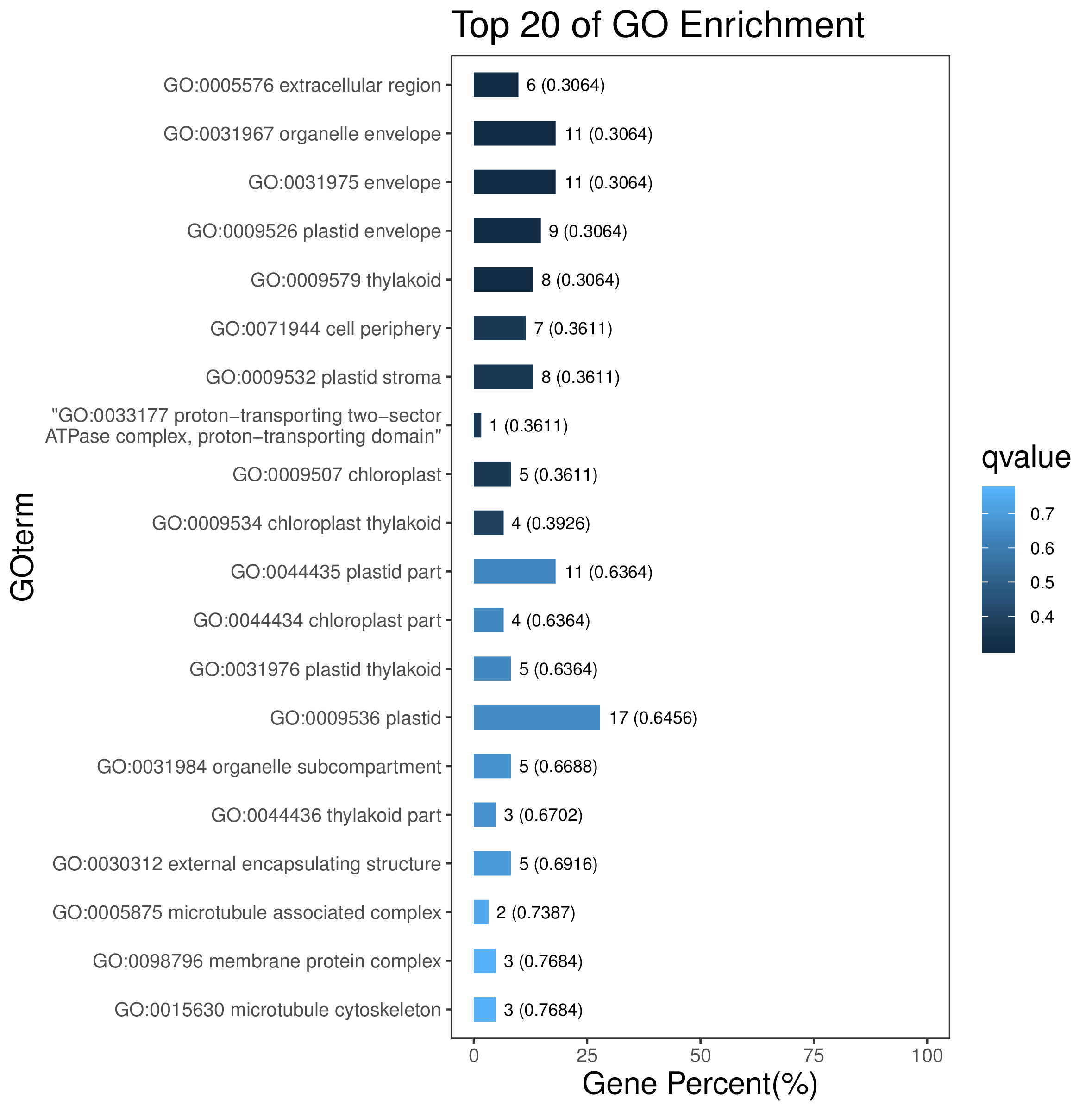
程序将按要求输出条形图,结果会生成png格式和PDF格式的图片。
输入文件:
选择文件输入类型:type1、type2或type3。根据输入文件的格式选择类型;输入的文件支持txt(制表符分隔)文本文件、csv(逗号分隔)文本文件、以及Excel专用的xlsx格式,同样支持旧版Excel的xls(Excel 97-2003 )格式。表格名称以字母、数字、下划线组成,不可以有后缀名称。
用于作图的行:选择想要展示的前n行富集结果,默认输出前20 行;
参数选择:P值或者Q值
顺序:条形图排列顺序,P/Q值从小到大排列绘图或P/Q值从大到小排列绘图;
类型:根据富集分析的数据库类型选择。
输出图片:
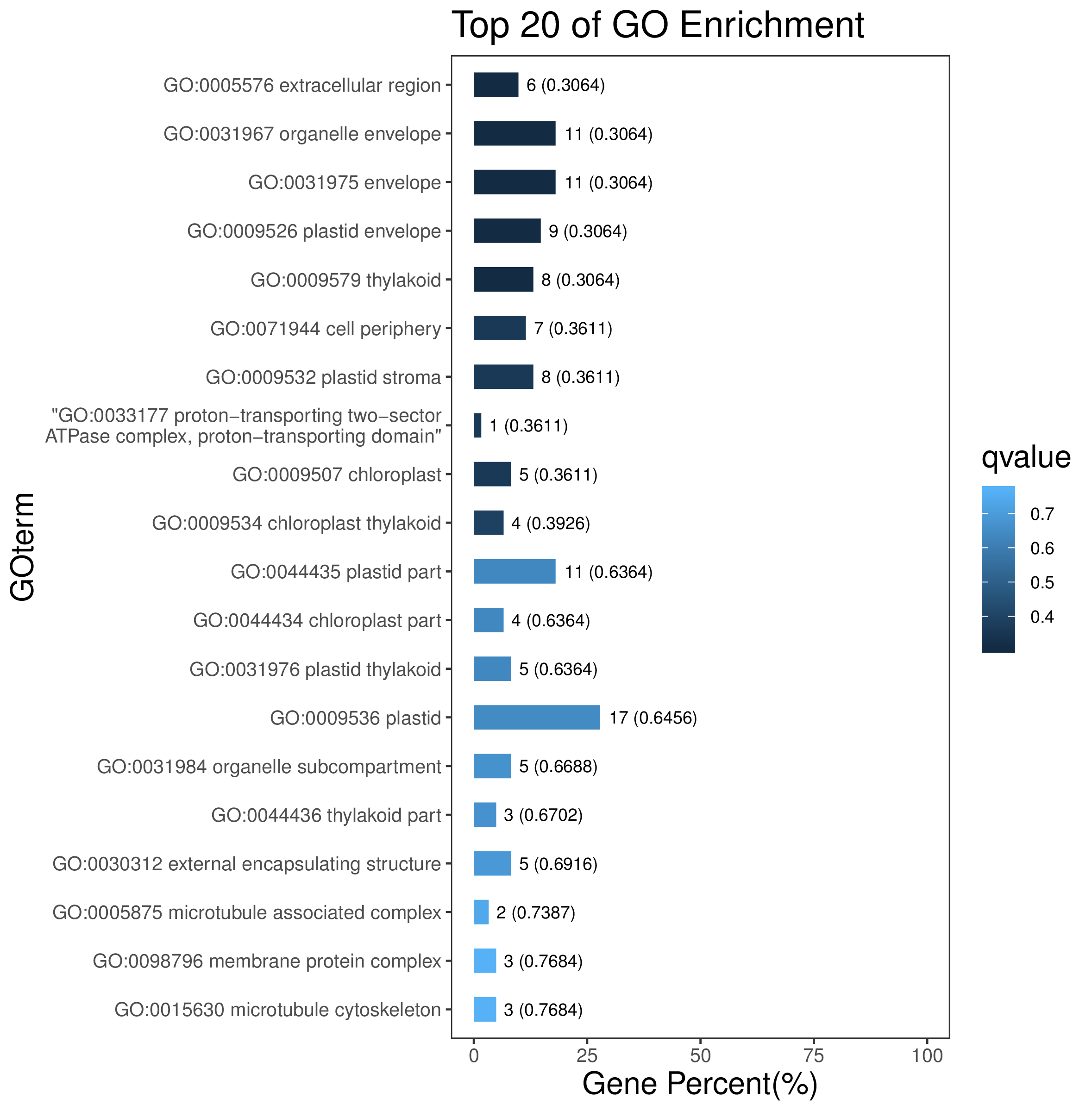
图片说明:纵坐标为Pathway/GOterm/DOterm/Reactome,横坐标为该Pathway/GOterm/DOterm/Reactome差异基因/目标基因数目占所有差异数目/目标基因数目的百分比,颜色越深P/Q值越小,柱子上的数值为该pathway数量及P/Q值。
Q1. 上传的数据需要保存成什么格式?文件名称和拓展名有没有要求?
OmicShare当前支持txt(制表符分隔)文本文件、csv(逗号分隔)文本文件、以及Excel专用的xlsx格式,同样支持旧版Excel的xls(Excel 97-2003 )格式。如果是核酸、蛋白序列文件,必须为FASTA格式(本质是文本文件)。
文件名可由英文和数字构成,文件拓展名没有限制,可以是“.txt”、“.xlsx”、“.xls”、“.csv”“.fasta”等,例如 mydata01.txt,gene02.xlsx 。
Q2. 提交时报错常见问题:
1.提交时显示X行X列空行/无数据,请先自查表格中是否存在空格或空行,需要删掉。
2.提交时显示列数只有1列,但表格数据不止1列:列间需要用分隔符隔开,先行检查文件是否用了分隔符。
其它提示报错,请先自行根据提示修改;如果仍然无法提交,可通过左侧导航栏的“联系客服”选项咨询OmicShare客服。
Q3. 提交的任务完成后却不出图该怎么办?
主要原因是上传的数据文件存在特殊符号所致。可参考以下建议逐一排查出错原因:
(1)数据中含中文字符,把中文改成英文;
(2) 数据中含特殊符号,例如 %、NA、+、-、()、空格、科学计数、罗马字母等,去掉特殊符号,将空值用数字“0”替换;
(3)检查数据中是否有空列、空行、重复的行、重复的列,特别是行名(一般为gene id)、列名(一般为样本名)出现重复值,如果有删掉。
排查完之后,重新上传数据、提交任务。如果仍然不出图,可通过左侧导航栏的“联系客服”选项咨询OmicShare客服。
Q4.下载的结果文件用什么软件打开?
OmicShare云平台的结果文件(例如,下图为KEGG富集分析的结果文件)包括两种类型:图片文件和文本文件。
图片文件:
为了便于用户对图片进行后期编辑,OmicShare同时提供位图(png)和矢量图(pdf、svg)两种类型的图片。对于矢量图,最常见的是pdf和svg格式,常用Ai(Adobe illustrator)等进行编辑。其中,svg格式的图片可用网页浏览器打开,也可直接在word、ppt中使用。
文本文件:
文本文件的拓展名主要有4种类型:“.os”、“.xls”、“.log”和“.txt”。这些文件本质上都是制表符分隔的文本文件,使用记事本、Notepad++、EditPlus、Excel等文本编辑器直接打开即可。结果文件中,拓展名为“.os”文件为上传的原始数据;“.xls”文件一般为分析生成的数据表格;“.log”文件为任务运行日志文件,便于检查任务出错原因。
Q5. 提交的任务一直在排队怎么办?
提交任务后都需要排队,1分钟后,点击“任务状态刷新”按钮即可。除了可能需运行数天的注释工具,一般工具数十秒即可出结果,如果超出30分钟仍无结果,请联系OS客服,发送任务编号给OmicShare客服,会有专人为你处理任务问题。
Q6. 结果页面窗口有问题,图表加载不出来怎么办?
尝试用谷歌浏览器登录OmicShare查看结果文件,部分浏览器可能不兼容。




 扫码支付更轻松
扫码支付更轻松


